| Autor |
Nachricht |
Tiffüü
Anmeldungsdatum: 18.03.2011
Beiträge: 91
|
 Verfasst am: 27. März 2011 21:33 Titel: Der genetische Code Verfasst am: 27. März 2011 21:33 Titel: Der genetische Code |
 |
|
Ich hab eine Klausuraufgabe gehabt, da sollte man einen Strang in Aminosäuren umschreiben.. ich weiß ja, das 3 Basen eine As ist.. nun sah der Strang aber irgendwie komisch aus :
GpppTAGCCTGAAATG ...
Die Basen hab ich mir jetzt ausgedacht..ich frage mich, was diese p's sein solln, und wie ich den Strang ablesen muss 
|
|
 |
Jaamar
Anmeldungsdatum: 14.06.2010
Beiträge: 119
|
|
 |
Tiffüü
Anmeldungsdatum: 18.03.2011
Beiträge: 91
|
 Verfasst am: 27. März 2011 21:48 Titel: Verfasst am: 27. März 2011 21:48 Titel: |
 |
|
achso .. das kann natürlich sein... also lass ich beim Ablesen das einfach weg dieses Gppp und fang ab dem nächste an 
|
|
 |
Jaamar
Anmeldungsdatum: 14.06.2010
Beiträge: 119
|
 Verfasst am: 27. März 2011 22:08 Titel: Verfasst am: 27. März 2011 22:08 Titel: |
 |
|
ach sry
nein, du fängst beim übersetzten beim startcodon an (AUG).
was mir noch gerade aufgefallen ist, dass du hier einen DNA-strang aufgeschrieben hast. bei der RNA ist das thymidin (T) durch ein uridin (U) ersetzt.
und ein DNA-strang ist nicht gecapped :-). das capping hat den sinn, dass die mRNA stabiler wird und es ist auch am transport der mRNA aus dem zellkern beteiligt.
hoffe das hilft ein bisschen weiter :-)
|
|
 |
Tiffüü
Anmeldungsdatum: 18.03.2011
Beiträge: 91
|
 Verfasst am: 27. März 2011 22:11 Titel: Verfasst am: 27. März 2011 22:11 Titel: |
 |
|
|
ja ich hab mir die basen ja auch nur ausgedacht.. mir ging es ja nur um diese p's.. also wenn ich ihn in aminosäuren umschreibe, lass ich Gppp einfach weg und fang dann normal mit den 3-er Sequenzen an .. ?
|
|
 |
Jaamar
Anmeldungsdatum: 14.06.2010
Beiträge: 119
|
 Verfasst am: 27. März 2011 22:23 Titel: Verfasst am: 27. März 2011 22:23 Titel: |
 |
|
Nein, die Translation erfolgt NUR im ORF (open reading frame).
Ein ORF beginnt immer mit einem Startcodon (AUG = Methionin; Adenosin-Urdidin-Guanin) und endet mit einem Stopcodon (UAG, UAA oder UGA).
Der restliche Teil der mRNA ist nicht codierend und wird vom Ribosom auch nicht in eine Aminosäuresequenz umgewandelt.
also:
blablabla AUG ...... UUA UAG blablabla
Met ....... Leu
Met = Methionin (genauer ein N-Formylmethionin, oder kurz fMet)
Leu = Leucin
blabla = nicht codierender Part der mRNA
Zuletzt bearbeitet von Jaamar am 29. März 2011 09:43, insgesamt einmal bearbeitet |
|
 |
Tiffüü
Anmeldungsdatum: 18.03.2011
Beiträge: 91
|
 Verfasst am: 27. März 2011 22:26 Titel: Verfasst am: 27. März 2011 22:26 Titel: |
 |
|
|
ja weis ich ja wenn dann halt da stand: GpppAUGCUGG... dann lass ich das Gppp weg und beginn mein Polypeptid mit Methionin ? also ich will nur wissen, ob das Gppp irgend ne Bedeutung für mich hat, wenn ich die Aufgabe lautet, ich soll die mRNA in As umschrieben..
|
|
 |
Jaamar
Anmeldungsdatum: 14.06.2010
Beiträge: 119
|
 Verfasst am: 27. März 2011 22:28 Titel: Verfasst am: 27. März 2011 22:28 Titel: |
 |
|
|
nein, in dem fall hat es das nicht :-)
|
|
 |
Tiffüü
Anmeldungsdatum: 18.03.2011
Beiträge: 91
|
 Verfasst am: 27. März 2011 22:34 Titel: Verfasst am: 27. März 2011 22:34 Titel: |
 |
|
ok 
|
|
 |
jörg

Anmeldungsdatum: 12.12.2010
Beiträge: 2107
Wohnort: Bückeburg
|
 Verfasst am: 28. März 2011 02:32 Titel: Verfasst am: 28. März 2011 02:32 Titel: |
 |
|
Entschuldigt die Einmischung, aber noch eine Ergänzung:
Ein Startcodon unmittelbar nach dem cap gelegen wird (sollte es sowas überhaupt geben) nicht gelesen.
Du beginnst also bei einem Startcodon in einiger Entfernung.
Sollten mehrere AUG- Triplets direkt aufeinanderfolgen, wird i.d.R. bei dem "letzten" (also dem 3'- gelegenen) mit der Translation begonnen.
_________________
RNA?- just another nucleic acid? |
|
 |
Tiffüü
Anmeldungsdatum: 18.03.2011
Beiträge: 91
|
 Verfasst am: 28. März 2011 23:41 Titel: Verfasst am: 28. März 2011 23:41 Titel: |
 |
|
ach echt ?? also wenn nach dem cap sofort ein AUG kommt, fang ich erst ab dem nächsten AUG an, das kommt.. und wenn nach dem cap irgend eine andere Sequenz kommt.. nehm ich dann gleich die, oder muss ich erst das AUG suchen ?? 
|
|
 |
jörg

Anmeldungsdatum: 12.12.2010
Beiträge: 2107
Wohnort: Bückeburg
|
 Verfasst am: 29. März 2011 00:07 Titel: Verfasst am: 29. März 2011 00:07 Titel: |
 |
|
Du suchst natürlich ein AUG, weil erst hier das Ribosom zu "lesen" beginnt.
Meist kommt nach dem cap eine UAC- Sequenz.
Ich weiss wieder mal nicht, worauf euer Dozent es mit solchen Aufgaben abzielt, denn normalerweise ist die 5'UTR (also ein nichttranslatierter regulatorischer Bereich vor -also 5'-wärts- des Startcodons) mind. 50- 100 Nukleotide lang (manchmal auch mehrere Tausend), dann erst kommt das Startcodon.
Das Ribosom (also seine 40S- Untereinheit) "scannt" die mRNA nämlich nach einer optimalen "Lage" ab.
Auch der Sequenzkontext, in dem das Startcodon sich befindet spielt dabei eine Rolle. Da gelten die sog. "Kozak- Regeln", nach denen der optimale Sequenzkontext für ein zu erkennendes Startcodon GCC ACC AUG G lautet.
Allerdings erfüllen dieses lediglich 5% der eukaryontischen mRNAs perfekt. Zu grosse Abweichungen von dieser Sequenz führen aber zu vermehrter Nichterkennung.
Damit hat auch der Sequenzkontext regulatorische Funktionen.
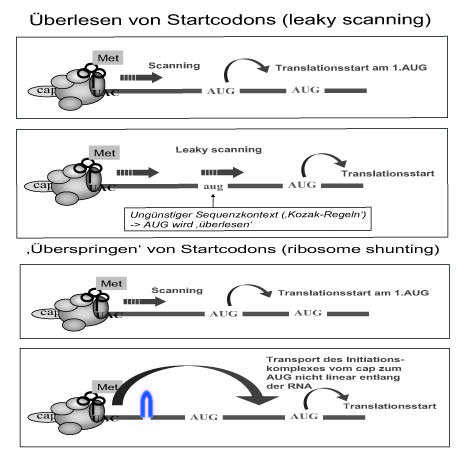
Aufeinanderfolgende AUG- Triplets fördern das "Überlesen" (leaky scanning, siehe unten), so dass erst am letzten "gestartet" wird oder sogar dahinter.
Ein AUG- Triplet in der 5'UTR ist dabei keinesfalls ungewöhnlich, beim Poliovirus existieren z.B. in einer 5'UTR sogar 7 nicht gelesene AUG- Triplets hintereinander in der "internal ribosome entry site" (IRES) unmittelbar vor dem "gewünschten" Startcodon.
In anderen Fällen können sie in Sekundärstrukturen untergebracht sein oder kurz dahinter. Auch dann werden sie vermehrt nicht- erkannt.
Falls dich das interessiert:
Es gibt dabei zwei Variationen des "Ribosomenverhaltens" (siehe auch angehängte Grafik):
1.) sog. "leaky scanning", also ein Startcodon wird nicht als solches erkannt, das Ribosom "überliest" es einfach, "läuft" dann die RNA weiter ab und benutzt das Startcodon, was einen günstigeren Sequenzkontext aufweist (Anwendung der "Kozak- Regeln"). Das gilt, wenn wie gesagt der Sequenzkontext ungünstig ist oder das Startcodon zu nahe am cap liegt.
2.) sog. "ribosome shunting", also der Transport des Initiationskomplexes erfolgt nicht- linear entlang der RNA zu dem Startcodon, das "gelesen werden soll". Das Ribosom "hüpft" da quasi hin. Hier bilden sich in der 5'UTR Sekundärstrukturen aus.
Kurz: Ich kenne keine eukaryontische mRNA, die über keine 5'UTR verfügt; zu kurze 5'UTRs führen zu womöglicher "Nichterkennung" des Startcodons, zu lange 5'UTRs wirken translationshemmend.
Und prokaryontische mRNAs haben nach meinem Wissen kein 5'cap.
Es kann aber auch sein, dass euer Dozent nur möchte, dass ihr wisst, dass Gppp das cap ist, obwohl das nach meiner Meinung ziemlich mindersinnig ist. Es könnte sich aber auch eine "Fangfrage" dahinter verbergen.
Kam die 5'UTR denn in der Vorlesung dran?
| Beschreibung: |
|
| Dateigröße: |
70.47 KB |
| Angeschaut: |
9261 mal |
|
_________________
RNA?- just another nucleic acid? |
|
 |
Tiffüü
Anmeldungsdatum: 18.03.2011
Beiträge: 91
|
 Verfasst am: 29. März 2011 00:23 Titel: Verfasst am: 29. März 2011 00:23 Titel: |
 |
|
Owee.. ich glaub nicht, das unser Dozent das so kompliziert meint.. es sind in der Klausur recht viele Fragen, wo ich mir denke, ob das ne Fangfrage sein soll, weil die zielich einfach sind..wie z.b mit den Kreuzungen wo man eine Testkreuzung macht und somit den Genotyp rausfindet ( fand ich sehr komisch) naja.. Ja wir haben nur den Aufbau eines Gens gehabt also 3'UTR (regulatory Region) und 5'UTR( Endpoint of transcription) diese beiden sind ja auch EXONS.. und dann halt, das die mRNA dann noch reifen muss (Spleißen) und dass am 3' Ende der Poly-A Schwanu hängt, und am 5' dann eben das cap.. mehr hatten wir dazu nicht.. ich denke mal, das er nur wissen möchte, das wir das mit dem cap kennen..
also such ich mir dann einfach das AUG und fange da an und wenns gleich nach dem cap kommt nehm ich das nächste.. da ausführlich hatten wir das nie 
|
|
 |
jörg

Anmeldungsdatum: 12.12.2010
Beiträge: 2107
Wohnort: Bückeburg
|
 Verfasst am: 29. März 2011 00:36 Titel: Verfasst am: 29. März 2011 00:36 Titel: |
 |
|
Wie angedeutet, ist es schwer einzuschätzen, was konkret bei solchen Aufgaben geprüft werden soll.
Gerade wenn es sich um ein Studium handelt und nicht um die Schule.
Ich wollte das nur anmerken, um zu erklären, warum du nicht direkt hinter dem cap anfängst mit der Translation und dass aufeinanderfolgende AUGs eine Falle sein könnten.
Ansonsten gilt die Regel: Geprüft wird, was Inhalt der Vorlesungen, Seminare und Praktika war.
Und sorry, ich wollte dich auch nicht verwirren oder verunsichern.....
_________________
RNA?- just another nucleic acid? |
|
 |
Tiffüü
Anmeldungsdatum: 18.03.2011
Beiträge: 91
|
 Verfasst am: 29. März 2011 00:40 Titel: Verfasst am: 29. März 2011 00:40 Titel: |
 |
|
|
ja stimmt schon und danke für die Erklärung aber so kompliziert war die Vorlesung nicht, nur dann halt die Klausurfragen.. ich werd das einfach so jetzt machen, wenns falsch ist, werd ichs chon ned durchfallen aber der har nie darüber gesprochen, was du mir grad erklärt hast ..
|
|
 |
jörg

Anmeldungsdatum: 12.12.2010
Beiträge: 2107
Wohnort: Bückeburg
|
 Verfasst am: 29. März 2011 00:42 Titel: Verfasst am: 29. März 2011 00:42 Titel: |
 |
|
Dann kommts vielleicht in Virologie oder so..... 
_________________
RNA?- just another nucleic acid? |
|
 |
Tiffüü
Anmeldungsdatum: 18.03.2011
Beiträge: 91
|
 Verfasst am: 29. März 2011 00:54 Titel: Verfasst am: 29. März 2011 00:54 Titel: |
 |
|
das weiss ich nicht .. hab ich das überhaupt  .. klingt aber jedenfalls ziemlich kompliziert.. naja falls ich das nochmal hab, weiss ich ja jetzt im Vorhinaus schon bescheid .. klingt aber jedenfalls ziemlich kompliziert.. naja falls ich das nochmal hab, weiss ich ja jetzt im Vorhinaus schon bescheid 
|
|
 |
|