| Autor |
Nachricht |
akvarel
Anmeldungsdatum: 06.02.2011
Beiträge: 11
|
 Verfasst am: 02. Nov 2011 10:49 Titel: Ähnlichkeit von Aminosäuren Verfasst am: 02. Nov 2011 10:49 Titel: Ähnlichkeit von Aminosäuren |
 |
|
Im Attachment ist das, was im Buch steht, ich verstehe aber nicht inwiefern sind Aminosäuren
Alanin und Threonin
Alanin und Serin
Asparagin und Glycin
Leucin und Phenylalanin
ähnlich?
Alanin ist unpolar, Threonin - polar
Alanin ist unpolar, Serin - polar
Aspargin - polar , Glycin unpolar ...
Und laut dem Buch Lysin und Phenylalanin sin nicht ähnlich, aber wieso sind dann Alanin und Threonin ähnlich??
| Beschreibung: |
|
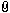
Download |
| Dateiname: |
blabla.jpg |
| Dateigröße: |
42.72 KB |
| Heruntergeladen: |
2932 mal |
|
|
 |
akvarel
Anmeldungsdatum: 06.02.2011
Beiträge: 11
|
 Verfasst am: 02. Nov 2011 10:57 Titel: Verfasst am: 02. Nov 2011 10:57 Titel: |
 |
|
Ich glaub ich habs.
Alanin, Threonin, Serin und Glycin sind einfach klein. Darin besteht ihre Ähnlichkeit. oder?
|
|
 |
134340

Anmeldungsdatum: 14.10.2011
Beiträge: 228
|
 Verfasst am: 02. Nov 2011 11:50 Titel: Verfasst am: 02. Nov 2011 11:50 Titel: |
 |
|
Schon ma bei wiki geguckt?
http://de.wikipedia.org/wiki/Alanin
http://de.wikipedia.org/wiki/Threonin
Zudem hab ich noch diesen Link ( http://www.guidobauersachs.de/oc/protein.html ) gefunden such dort mal unter "Aminosäuren mit aliphatischen Hydroxylgruppen". Dort steht folgendes dazu
| Zitat: | Zwei AS, Serin und Threonin, besitzen aliphatische Hydroxylgruppen.
Serin ist im Prinzip ein hydroxyliertes Alanin, Threonin ein hydroxyliertes Valin. Die Hydroxylgruppen machen Serin und Threonin aber sehr viel hydrophiler (also "wasserfreundlicher") und reaktiver als Alanin und Valin. |
Also alle deine Aminosäuren besitzen im Prinziep den gleichen Grundaufbau und man kann sie leicht in eine der anderen "ähnlichen" Aminosäuren überführen.
_________________
Naive Fragen zu stellen ist überhaupt eine der erfolgreichsten Methoden, um voranzukommen. Craig Venter |
|
 |
PaGe
Moderator

Anmeldungsdatum: 19.03.2007
Beiträge: 3549
Wohnort: Hannover
|
 Verfasst am: 02. Nov 2011 20:22 Titel: Verfasst am: 02. Nov 2011 20:22 Titel: |
 |
|
Die Größe wäre eine Idee, wobei da schon 1-2 C-Atome Unterschied bestehen. Und wie du schon richtig erkannt hast, sind die EIgenschaften eigentlich völlig anders. Daher bleibt es wahrscheinlich das Geheimnis des Autors worin die Gemeinsamkeit besteht.
_________________
Die deutsche Rechtschreibung ist Freeware, du darfst sie kostenlos nutzen. Aber sie ist nicht Open Source, d. h., du darfst sie nicht verändern oder in veränderter Form veröffentlichen. |
|
 |
134340

Anmeldungsdatum: 14.10.2011
Beiträge: 228
|
 Verfasst am: 03. Nov 2011 14:27 Titel: Verfasst am: 03. Nov 2011 14:27 Titel: |
 |
|
ich denke ich habs 
Ich hab noch mal überlegt ob nicht vielleicht die DNA-sequenzierung der verschiedenen Aminosäuren gemeint ist und ich denke ich hatte recht.
Hier die Aminosäurensequenzen:
Alanin 5' GCG 3'
Alanin 5' GCA 3'
Alanin 5' GCC 3'
Alanin 5' GCU 3'
Threonin 5' ACG 3'
Threonin 5' ACA 3'
Threonin 5' ACC 3'
Threonin 5' ACU 3'
Was fällt dir bei Alanin und Threonin auf?
Hier die sequenzierung von Serin und Glycin:
Serin 5' UCG 3'
Serin 5' UCA 3'
Serin 5' UCC 3'
Serin 5' UCU 3'
Glycin 5' GGG 3'
Glycin 5' GGA 3'
Glycin 5' GGC 3'
Glycin 5' GGU 3'
Allerdings finde ich bei Serin und Glycin keine kongruenz.
_________________
Naive Fragen zu stellen ist überhaupt eine der erfolgreichsten Methoden, um voranzukommen. Craig Venter |
|
 |
Firelion

Anmeldungsdatum: 27.08.2009
Beiträge: 1878
|
 Verfasst am: 03. Nov 2011 15:24 Titel: Verfasst am: 03. Nov 2011 15:24 Titel: |
 |
|
Hi,
hmm wir haben gelernt, dass es bei Alignments darauf ankommt, dass entweder die Basen identisch oder von den Eigenschaften ihrer Seitenketten sehr ähnlich sind. Sonst ist es wahrscheinlicher, dass mal eine AS dazu gekommen oder weggelöscht wurde.
Das hat mit der Funktionalität des späteren Proteins zu tun: Ersetzt du eine hydrophile gegen eine hydrophobe AS ist mit einer höheren Wahrscheinlichkeit die Funktion des Proteins wegen der Fehlfaltung futsch. Ersetzt du aber Isoleucin gegen Leucin oder umgekehrt beeinträchtigt, dass die Funktion weniger. Lsut Bioinformatikvorlesung liegt das Einfügen/ Rausnehmren von AS irgendwo dazwischen.
Fürs Sequencealignment bewertet (scort) man dann das Alignment um das Beste zufinden. Da hat dann jedes Match einen bestimmten + Wert (je nach AS verschieden) und Minuspunkte gibt es für (InDels betzw Mismatch (jedes Mismatch verschieden).
Es kann sein, dass ich mich irre, aber mir erschließt sich nicht hganz warum der Autor es für wichtig hält dass die Codons ähnlich sind.
Das einzige was ich mir denbkrn könnte ist dass es um Wobble geht.
Aber auch das ist unwahrscheinlich, da soweit ich weiß bei der Wobble Hypothese die ersten zwei Basen des Tripplett entscheidend sind.
Laut den Beispiel Scoring Matrices im ,, understanding bioinformatics" -von Zvelebil/Baum.
gibt bedeutet Missmatch
und Serin/ Alanin : 0
Serin/Threonin: 0
Asparagin/Glycin :0
Leucin/ Phenylalanin: 0
Laut BLOSUM- 62 Matrix
und Laut PAM120:
S/A :+1
S/T : +2
N/G : 0
L/ F : 0
Also gibt es wenig Penalty für einen Missmatch.
Vielleicht meinte der Autor das so ?
Die Werte reichen in der ersten Matrix von - 4 bis 9
und in der zweiten von - 8 - 12
Also ist ein austausch weder extrem gut für die Richtigkeit des Alignments noch ein Indikator für ein schlechtes....
LG Firelion
_________________
It is well known that a vital ingredient of success is not knowing that what youre attempting cant be done - Terry Pratchett |
|
 |
PaGe
Moderator

Anmeldungsdatum: 19.03.2007
Beiträge: 3549
Wohnort: Hannover
|
 Verfasst am: 03. Nov 2011 16:10 Titel: Verfasst am: 03. Nov 2011 16:10 Titel: |
 |
|
Ich finde es aber etwas strange, wenn man aminosäuresequenzen vergleicht, auf die dna-ebene zu switchen. Dann sollte man gleich die dna-sequenzen vergleichen. Es geht doch viel mehr um die funktionalität des proteins. Wenn allerdings programme ebenfalls geringe mali vergeben, müste es entweder empirisch festgestellt oder doch irgendwie zu erklären ist. E8nfach einen evolutionsbiologen oder ein entsprechendes buch fragen.
_________________
Die deutsche Rechtschreibung ist Freeware, du darfst sie kostenlos nutzen. Aber sie ist nicht Open Source, d. h., du darfst sie nicht verändern oder in veränderter Form veröffentlichen. |
|
 |
134340

Anmeldungsdatum: 14.10.2011
Beiträge: 228
|
 Verfasst am: 03. Nov 2011 16:50 Titel: Verfasst am: 03. Nov 2011 16:50 Titel: |
 |
|
| PaGe hat Folgendes geschrieben: | | Ich finde es aber etwas strange, wenn man aminosäuresequenzen vergleicht, auf die dna-ebene zu switchen. Dann sollte man gleich die dna-sequenzen vergleichen. Es geht doch viel mehr um die funktionalität des proteins. |
Meinst du damit meinen Post?
_________________
Naive Fragen zu stellen ist überhaupt eine der erfolgreichsten Methoden, um voranzukommen. Craig Venter |
|
 |
PaGe
Moderator

Anmeldungsdatum: 19.03.2007
Beiträge: 3549
Wohnort: Hannover
|
 Verfasst am: 03. Nov 2011 21:45 Titel: Verfasst am: 03. Nov 2011 21:45 Titel: |
 |
|
Ich will damit nur sagen, dass ich das für unwahrscheinlich halte. Sollte es dennoch die Antwort sein, hat der Autor des Buchs wenig Ahnung davon, wie man wissenschaftlich arbeitet.
_________________
Die deutsche Rechtschreibung ist Freeware, du darfst sie kostenlos nutzen. Aber sie ist nicht Open Source, d. h., du darfst sie nicht verändern oder in veränderter Form veröffentlichen. |
|
 |
134340

Anmeldungsdatum: 14.10.2011
Beiträge: 228
|
 Verfasst am: 04. Nov 2011 07:50 Titel: Verfasst am: 04. Nov 2011 07:50 Titel: |
 |
|
| PaGe hat Folgendes geschrieben: | | Ich will damit nur sagen, dass ich das für unwahrscheinlich halte. Sollte es dennoch die Antwort sein, hat der Autor des Buchs wenig Ahnung davon, wie man wissenschaftlich arbeitet. |
Achso.
Ich hab einfach nur überlegt, was der Autor meinen könnte und da bin ich eben auf die DNA-sequenzen gekommen, auch wenn das vielleicht wie du schon richtig anmerktest, etwas weit hergeholt ist. Aber ich kenn ja den Autor nicht, also kann ich genau wie ihr nur spekulieren.
_________________
Naive Fragen zu stellen ist überhaupt eine der erfolgreichsten Methoden, um voranzukommen. Craig Venter |
|
 |
|