| Autor |
Nachricht |
MagicAnna
Anmeldungsdatum: 31.08.2007
Beiträge: 4
|
 Verfasst am: 20. Jan 2008 17:05 Titel: PCR - Fragen (Facharbeit) Verfasst am: 20. Jan 2008 17:05 Titel: PCR - Fragen (Facharbeit) |
 |
|
Hallo!
Ich habe meine Facharbeit über "PCR-Anwendungsmöglichkeiten in der Medizin und Kriminalistik" geschrieben und sie auch schon abgegeben. Nächste Woche werde ich wahrscheinlich meine mündliche Prüfung darüber haben. Ich habe mir jetzt die ganzen Sachen nocheinmal angeschaut, doch eine Frage ist mir bis jetzt ungeklärt geblieben. Ich hab sie hier schon mal gestellt, aber niemand konnte sie mir beantworten.
1.) Gibt man bei der PCR nur eine bestimmte Sorte des Primers hinzu oder unterschiedliche? Ansonsten kann ich mir es nicht erklären, warum die PCR-Produkte bei der Elektrophorese nach Größen aufgetrennt werden, wenn doch nur eine bestimmte Sequenz amplifiziert wird. Ich frage mich nur, woher ich die unterschiedlich lange Fragmente nach der PCR herkommen.
2.) Es werden öfters vier unterschiedliche Farben hinzugegeben, damit man sie bei der Analyse erkennt. Nun frage ich mich, warum ich unterschiedliche Farben hab? Stellt eine Farbe eine bestimme Länge der Basen dar oder die jeweiligen Nukleotiden? Und wozu Farben? Was sagen sie dann aus?
3.) Warum verwendet man beim Genetischen Fingerabdruck Restriktionsenzyme? Die sind doch überflüssig, wenn ich die PCR mache, da ich die gesuchte Sequenz sowieso durch Anlagerung der Primer bekomme.
Ich hoffe, ihr könnt mir da weiterhelfen, auch, wenn ihr nur eine Frage beantworten könnt,ist ziemlich dringend!
Vielen Dank im Voraus! Anna
|
|
 |
revilo
Anmeldungsdatum: 13.12.2007
Beiträge: 79
|
 Verfasst am: 20. Jan 2008 18:50 Titel: Verfasst am: 20. Jan 2008 18:50 Titel: |
 |
|
1.) Gibt man bei der PCR nur eine bestimmte Sorte des Primers hinzu oder unterschiedliche?
Man gibt einen Vorwärts-und einen Rückwärtsprimer zu dem Reaktionsgemisch hinzu. Wenn du das gleiche Gen bei unterschiedlichen Menschen durch PCR amplifizierst, sind die resultierenden PCR-Prdukte gleich groß (Unterschiede bezüglich der Nukleotid-Sequenz kannst du ja nicht anhand der Fragmentgröße erkennen).
Wenn du unterschiedlich große Fragmente bekommst kann das mehrere Ursachen haben:
Es gibt Gene, die nicht als Einzelkopie vorliegen, diese Gene können sich in ihrer Länge unterscheiden.
Der Mensch ist diploid, wenn bei einem Chromosom Mutationen stattgefunden haben (Duplikation, Deletion, Translokation oder Inversion) können auch unterschiedlich große Fragmente bei einer PCR entstehen.
2.) Was meinst du mit Farben ?
Die Nukleotide können mit unterschiedlichen Fluoreszenzfarbstoffen gekoppelt sein, damit man die Sequenzierreaktion spektroskopisch auswerten kann, dann besitzt jedes Nukleotid eine andere fluoreszierende Gruppe.
3.) Warum verwendet man beim Genetischen Fingerabdruck Restriktionsenzyme? Die sind doch überflüssig, wenn ich die PCR mache, da ich die gesuchte Sequenz sowieso durch Anlagerung der Primer bekomme.
Den ersten Teil hast du beantwortet: Die PCR ist dazu da, um die DNA zu vermehren. Die Restriktionsenzyme sind dazu da, um Unterschiede in der Sequenz festzustellen. Restriktionsenzyme schneiden die DNA an bestimmten Erkennungssequenzen. Die Erkennungssequenz umfasst die Abfolge mehrerer Nukleotide. Wenn du zwei Proben hast, die sich in den Schnittmustern unterscheiden, deutet dies auf Mutationen in den Erkennungssequenzen hin. Du hast dann die DNA von zwei verschiedenen Probanden amplifiziert.
|
|
 |
nangillala
Anmeldungsdatum: 20.01.2008
Beiträge: 11
|
 Verfasst am: 20. Jan 2008 18:54 Titel: Re: PCR - Fragen (Facharbeit) Verfasst am: 20. Jan 2008 18:54 Titel: Re: PCR - Fragen (Facharbeit) |
 |
|
Hi Anna,
interessantes Thema hast du dir ausgesucht. Hier mal meine Vorschläge ohne Garantie auf Richtigkeit:
| MagicAnna hat Folgendes geschrieben: |
1.) Gibt man bei der PCR nur eine bestimmte Sorte des Primers hinzu oder unterschiedliche? Ansonsten kann ich mir es nicht erklären, warum die PCR-Produkte bei der Elektrophorese nach Größen aufgetrennt werden, wenn doch nur eine bestimmte Sequenz amplifiziert wird. Ich frage mich nur, woher ich die unterschiedlich lange Fragmente nach der PCR herkommen.
|
Man gibt immer zwei Primer hinzu, einen für den Hin- einen für den Rückstrang. Je nachdem wonach man sucht nutzt man andere Primer. Wenn ich nach einem ganz bestimmten Gen suche nutze ich einen Primer, der möglichst spezifisch an den Anfang des Gens oder noch davor bindet. Es gibt aber auch universal-Primer. Hier wird einfach versucht möglichst die gesamte DNA zu amplifizieren. Beim Kriminalistik-Beispiel könnte ich mir auch gut vorstellen, dass das so gemacht wird, da man ja oft nur geringe Mengen DNA findet. Danach werden meines Wissens nach Minisatelliten untersucht.
| MagicAnna hat Folgendes geschrieben: |
2.) Es werden öfters vier unterschiedliche Farben hinzugegeben, damit man sie bei der Analyse erkennt. Nun frage ich mich, warum ich unterschiedliche Farben hab? Stellt eine Farbe eine bestimme Länge der Basen dar oder die jeweiligen Nukleotiden? Und wozu Farben? Was sagen sie dann aus?
|
Die Farben werden nur hinzugegeben, wenn später eine Sequenzierung erfolgen soll. Jedes Nukleotid hat seine eigene Farbe (dass die eine bestimmte Bedeutung haben wage ich mal zu bezweifeln). Wenn du die DNA nun an einem Detektor vorbeiführst, so kann die Nukleotidfolge abgelesen werden.
Es kann aber auch sein, dass du andere Sequenziermethoden meinst:
1.Sanger Sequenzierung: Hier werden ddNTPs hinzugegeben, die dafür sorgen, dass der Strang nicht weiter verlängert werden kann. Es wird immer nur ein Ansatz pro ddNTP gemacht, später kann man mit Hilfe der Gelelektrophorese die Sequenz erstellen. Die ddNTPs werden oft farbig dargestellt, vielleicht meinst du also das.
2. Beim Pyrosequencing werden nacheinander die Nukleotide in den Ansatz gegeben. "Passt" das Nukleotid gibt es einen Lichtblitz (durch die Luciferase) und du bekommst so die Sequenz heraus.
| MagicAnna hat Folgendes geschrieben: |
3.) Warum verwendet man beim Genetischen Fingerabdruck Restriktionsenzyme? Die sind doch überflüssig, wenn ich die PCR mache, da ich die gesuchte Sequenz sowieso durch Anlagerung der Primer bekomme.
|
Das hängt mit 1) zusammen. Man könnte natürlich probieren nur bestimmte Gene zu amplifizieren, jedoch ist hier auch dementsprechend die Wahrscheinlichkeit größer, dass du eben jenen kurzen Abschnitt nicht gut sequenziert bekommst o.ä. Zudem dürften Universal-Primer günstiger sein. Der Mensch unterscheidet sich auch eher in der sog. Junk-DNA, die keine Gene trägt. Natürlich unterscheidet man sich auch in Genen, da diese aber oft Lebensnotwendig sind ist hier nicht so viel Spielraum gegeben wie auf den Abschnitten der DNA, welche nicht für Gene kodieren. Da weißt du mehr über die Methoden als ich. Restriktionsfragmente werden jedenfalls benutzt um den sog. genetischen Fingerabdruck zu erlangen, da sie ganz spezielle Schnittmuster haben, die dann in Kombination immer einmalig sind. Stell dir das so vor (Theorie meinerseits, ich weiß nicht wie es die Kriminalmenschen wirklich machen): Du weißt, dass ein Minisatellit sehr selten ist, und du hast ein Enzym welches genau hier spaltet. Schon kannst du schnell erkennen ob deine Probe selbigen beinhaltet. Man kombiniert dann vermutlich einige Enzyme et voila. Der Vorteil liegt darin, dass man Enzyme meist eh an der Hand hat und nicht wie Primer erst herstellen (lassen) muss. Restriktion wird auch verwendet, da du ja nicht immer genau weißt wo aufgehört wrid zu synthetisieren. Du kannst also Satelliten-DNA amplifizieren, dir den Teil herausschneiden, der dich interessiert (bspw. die Wiederholung von AG o.ä.) und musst dann nur noch einen Fragmentlängenvergleich machen. Das nennt man dann Restriktionsfragmentlängenpolymorphismus (RFLP)
Aber wie gesagt: Alles meine Erklärungen die nicht unbedingt stimmen müssen, da ich nicht weiß wie es in der Kriminalistik gemacht wird.
|
|
 |
MagicAnna
Anmeldungsdatum: 31.08.2007
Beiträge: 4
|
 Verfasst am: 21. Jan 2008 20:29 Titel: Verfasst am: 21. Jan 2008 20:29 Titel: |
 |
|
Ich verstehe aber immer noch nicht, woher die unterschiedlichen Längen der Amplifikate nach einer PCR herkommen??? Während einer Elektrophorese werden diese ja nach Größe aufgetrennt, aber wie geht das, wenn die PCR Produkte sowieso alle gleich lang bzw. groß sind??
Okay, nehmen wir jetzt mal an, die Nukleotiden werden jetzt mit der jeweiligen Farben markiert, fluoresziert und so erkennt man sie dann bei der Sequenzierung. Nun frage ich mich aber, wenn ich mir zB die Auswertung eines Vaterschaftstestes ansehe, wie z.B. alle vier Farben an einer Stelle gleichzeitig auftreten können? Ich meine, wenn ich jetzt bei Nukleotid T angelangt bin, das meinetwegen mit der Farbe rot markiert ist, dann sollte auch nur an dieser Stelle ein Peak oder sonstwas angezeigt werden. Doch oftmals werden mehrere auf einmal gezeigt. (Ich schick im Anhang was mit, damit ihr versteht, was ich meine)
Manchmal werden auch nur einfach zwei Farben angegeben. Ich hoffe, ihr versteht mein Problem.
Die anderen Sachen habe ich jetzt verstanden, herzlichen Dank an die Antworter ;-)
LG Anna
| Beschreibung: |
|
Download |
| Dateiname: |
vaterschaft_abb1.jpg |
| Dateigröße: |
54.46 KB |
| Heruntergeladen: |
3100 mal |
| Beschreibung: |
| Hier ist die Auswertung des Vaterschaftstestes durch die Kapillarelektrophorese. |
|
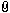
Download |
| Dateiname: |
PICT0476_800x600.JPG |
| Dateigröße: |
77.45 KB |
| Heruntergeladen: |
3099 mal |
|
|
 |
|
|